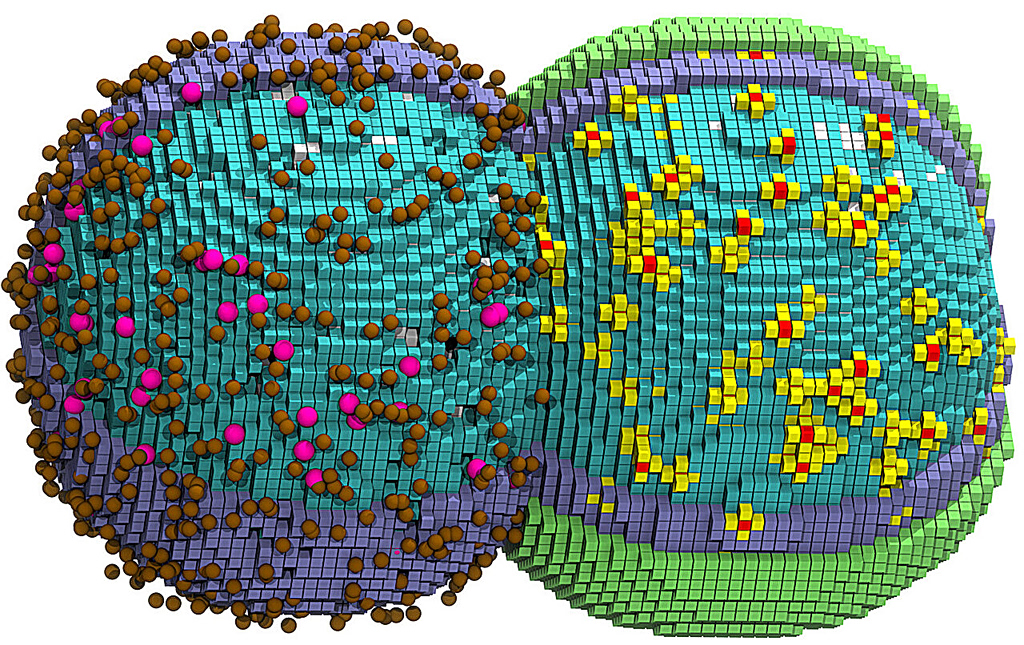
Μια ομάδα ερευνητών προσομοίωσε για πρώτη φορά τον πλήρη κύκλο ζωής ενός ζωντανού βακτηριακού κυττάρου σε ανάλυση νανοκλίμακας, παρακολουθώντας κάθε γονίδιο, πρωτεΐνη, μόριο RNA και χημική αντίδραση από την αναπαραγωγή του DNA έως την κυτταρική διαίρεση. Η μελέτη, που δημοσιεύτηκε στις 9 Μαρτίου στο επιστημονικό περιοδικό Cell, σηματοδοτεί ένα νέο ορόσημο στην υπολογιστική βιολογία και προσφέρει ένα εργαλείο ικανό να αντικαταστήσει εκατοντάδες εργαστηριακά πειράματα ταυτόχρονα.
Υπό την καθοδήγηση της καθηγήτριας χημείας Zan Luthey-Schulten στο Πανεπιστήμιο του Ιλινόις Urbana-Champaign, η ερευνητική ομάδα επέλεξε το JCVI-syn3A — έναν συνθετικό οργανισμό που δημιουργήθηκε στο J. Craig Venter Institute στην Καλιφόρνια. Το κύτταρο αυτό διαθέτει λιγότερα από 500 γονίδια σε ένα μοναδικό κυκλικό χρωμόσωμα και είναι γνωστό ανεπίσημα ως Syn3A.
Το Syn3A περιλαμβάνει μόνο τα γονίδια που είναι απαραίτητα για την αναπαραγωγή, την ανάπτυξη, τη διαίρεση και τις βασικές κυτταρικές λειτουργίες, γεγονός που το καθιστά ιδανικό υποψήφιο για τη μοντελοποίηση ενός ολόκληρου κυττάρου. Το αποτέλεσμα ήταν ένα τρισδιάστατο, πλήρως δυναμικό κινητικό μοντέλο που απεικονίζει τον κύκλο περίπου 105 λεπτών του κυττάρου σε τέσσερις διαστάσεις — τρεις χωρικές και μία χρονική. «Πρόκειται για ένα τρισδιάστατο, πλήρως δυναμικό κινητικό μοντέλο ενός ζωντανού ελάχιστου κυττάρου που μιμείται αυτό που συμβαίνει στο πραγματικό κύτταρο», δήλωσε η Luthey-Schulten.
Η εκτέλεση της προσομοίωσης αποδείχθηκε μια τεράστια υπολογιστική πρόκληση. Ο μεταπτυχιακός φοιτητής Andrew Maytin διαπίστωσε ότι η μοντελοποίηση μόνο της αντιγραφής του χρωμοσώματος σχεδόν διπλασίαζε τον συνολικό χρόνο επεξεργασίας. Για να αντιμετωπίσει το πρόβλημα, αφιέρωσε μία μονάδα επεξεργασίας γραφικών (GPU) αποκλειστικά στην αντιγραφή του DNA, ενώ μια δεύτερη GPU χειριζόταν όλες τις υπόλοιπες κυτταρικές διεργασίες.
Με αυτή τη μέθοδο, η προσομοίωση ενός πλήρους κυτταρικού κύκλου χρειάστηκε έξι ημέρες στον υπερυπολογιστή Delta, που υποστηρίζεται από το NSF στο Εθνικό Κέντρο Εφαρμογών Υπερυπολογιστών του πανεπιστημίου. «Δεν μπορώ να υπερτονίσω πόσο δύσκολο είναι να προσομοιώσεις πράγματα που κινούνται — και να το κάνεις αυτό σε 3D για ολόκληρο κύτταρο ήταν… θριαμβευτικό», δήλωσε ο Zane Thornburg, μεταδιδακτορικός ερευνητής στο Ινστιτούτο Beckman που συμμετείχε στο έργο.
Παρά τους περιορισμούς του — το μοντέλο υπολογίζει τον μέσο όρο της δυναμικής των μορίων αντί να προσομοιώνει άτομο προς άτομο — η προσομοίωση αποδείχθηκε εξαιρετικά ακριβής. Σε επαναλαμβανόμενες εκτελέσεις με ελαφρώς διαφορετικές αρχικές συνθήκες, ο προσομοιωμένος κυτταρικός κύκλος ταίριαζε με τον πραγματικό χρόνο λειτουργίας με ακρίβεια δύο λεπτών.
Στην εργασία συμμετείχαν επίσης οι Angad Mehta από το Πανεπιστήμιο του Ιλινόις, Taekjip Ha από το Boston Children’s Hospital και τη Ιατρική Σχολή του Harvard, καθώς και ο John Glass από το J. Craig Venter Institute. Η μελέτη ανοίγει τον δρόμο για τη διεξαγωγή εικονικών πειραμάτων μεγάλης κλίμακας, προσφέροντας, όπως σημειώνει η Luthey-Schulten, τη δυνατότητα «να λάβεις τα αποτελέσματα εκατοντάδων πειραμάτων ταυτόχρονα».